Biochip permite sequenciar moléculas grandes de DNA
Redação do Site Inovação Tecnológica - 11/01/2010
[Imagem: Nature Nanotechnology]
Pesquisadores da Universidade de Boston, nos Estados Unidos, desenvolveram uma tecnologia para sequenciar genomas mais rapidamente e com menor custo.
A novidade reduz dramaticamente a quantidade de DNA necessária para o sequenciamento, eliminando a fase de amplificação de DNA, que é cara, demorada e sujeita a erros.
No buraco da agulha
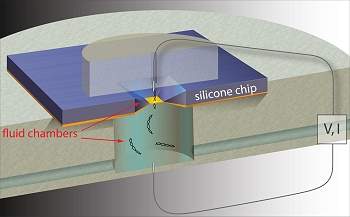
A técnica consiste em detectar moléculas de DNA à medida que elas passam por nanoporos de silício no interior de um biochip.
Campos elétricos são usados para inserir longas fitas de DNA através de poros cujos diâmetros medem apenas 4 nanômetros de largura, de forma parecida com passar uma linha pelo buraco de uma agulha.
A seguir, medições ultra sensíveis das correntes elétricas que atravessam o biochip são usadas para detectar cada molécula de DNA à medida que ela passa pelo nanoporo.
Fotocópias moleculares
"A fase atual da pesquisa indica que podemos detectar quantidades muito menores de amostras de DNA do que se havia conseguido antes. Quando pesquisadores começarem a implementar o sequenciamento de genomas ou a obtenção de perfis genômicos usando nanoporos, eles poderão usar nossa abordagem para reduzir enormemente o número de cópias usadas nessas medições", disse Amit Meller, coordenador do grupo.
Atualmente, o sequenciamento de genomas usa a amplificação de DNA para fazer bilhões de cópias moleculares, criando uma amostra grande o suficiente para ser analisada. Além do tempo e do custo desse processo, algumas das moléculas - que são como fotocópias de fotocópias - não saem perfeitas.
Fitas de DNA mais longas
A nova técnica usa campos elétricos circulando pelo bocal de entrada dos nanoporos para atrair fitas grandes de DNA, com carga elétrica negativa, fazendo-as passar pelos orifícios, onde a sequência de DNA pode ser lida. Como o DNA é atraído para os nanoporos a distância, poucas cópias da molécula são necessárias para que a análise possa ser feita.
"As tecnologias atuais de amplificação de DNA limitam o comprimento da molécula a ser utilizada a menos de mil pares de base. Como nosso método elimina a amplificação, ele não apenas reduz o custo, o tempo e a taxa de erros como também permite que a análise seja feita em fitas de DNA muito longas, muito maiores do que as usadas atualmente," afirmou Meller.
Espaguete e nanotecnologia
A técnica se tornou possível graças a uma descoberta surpreendente feita pelas cientistas: quanto mais longa a fita de DNA, mais rapidamente ele "encontra" a abertura do nanoporo.
"Isto é realmente surpreendente. Seria de se esperar que, se você tem um 'espaguete' mais longo, então achar sua ponta seria muito mais difícil," diz Meller. Contudo, como virtualmente tudo em nanoescala, a eletrofísica das dimensões nanométricas também apresenta regras e comportamentos que contrariam a experiência do mundo macroscópico.
Artigo: Electrostatic Focusing of Unlabelled DNA into Nanoscale Pores Using a Salt Gradient
Autores: Meni Wanunu, Will Morrison, Yitzhak Rabin, Alexander Y. Grosberg, Amit Meller
Revista: Nature Nanotechnology
Data: 20 December 2009
Vol.: Published online before print
DOI: 10.1038/nnano.2009.379


Hidrogênio poderá ser coletado por mineração, com custo mínimo
Fita adesiva comum tem memória útil até para computação
Dissipador de cobre otimizado derruba consumo de energia dos computadores
Novo tipo de magnetismo dá impulso definitivo à computação magnética
Computador quântico de luz tritura recorde de velocidade
Menor energia já medida permitirá contar fótons um por um
Nova técnica reprograma a matéria rearranjando rapidamente seus átomos
Computador alternativo de silício resolve problemas intratáveis hoje
Plumas de vapor na lua Europa são contestadas por novos dados
Como levantar 2.500 toneladas sem precisar de um guindaste
Cientistas criam biorrobô vivo com sistema nervoso primitivo
Para extrair energia osmótica, basta lubrificar o filtro
Barreiras de luz controlam fluxo de fluido em três dimensões
Iontrônica: Chip nanofluídico tem memória semelhante à do cérebro
Chip filma e controla reação química em tempo real
Esculpir a água permite formar relevos líquidos
Todos os direitos reservados.
É proibida a reprodução total ou parcial, por qualquer meio, sem prévia autorização por escrito.